文章题目:![]()
Telomere-to-telomere and gap-free reference genome assembly of the kiwifruit Actinidia chinensis
文章杂志:Horticulture Research
影响因子:7.291
研究背景:
猕猴桃是一种滕本科水果,因其高维生素C含量和美味的口感,被誉为“水果之王”,具有重要的经济价值。近年来,公布了多个品种的猕猴桃基因组,促进了猕猴桃功能基因组学的发展。但仍然存在大量未锚定的序列和gaps,特别是在高重复区域。因此,对于高质量参考基因组的组装和注释对猕猴桃重要农艺性状的功能基因组学研究和全基因组分子设计育种极具意义。
材料与方法:
本研究中,选择中国广泛栽培的优良猕猴桃品种——“红阳”(Actinidia chinensis cv. ‘Hongyang’)作为研究材料进行相关测序,其中:PacBio HiFi 数据31.9 Gb(52×)、ONT ultra-long 19.0 Gb(31×)和Hi-C 93.1Gb(150×)。
研究结果:
1. 构建猕猴桃T2T基因组
使用PacBio-HiFi读数来组装染色体规模的基因组,并结合ONT超长读数来填补空白。在组装过程中,为避免Hi-C数据带来新的间隙和错误的连接,作者使用了自己编写的Perl脚本(https://github.com/aaranyue/CTGA,使用Ref-guided策略重新绘制了HiFi重叠群与假染色体的关系。最终实现了两套染色体水平和无间隙的单倍型,HY4P和HY4A。
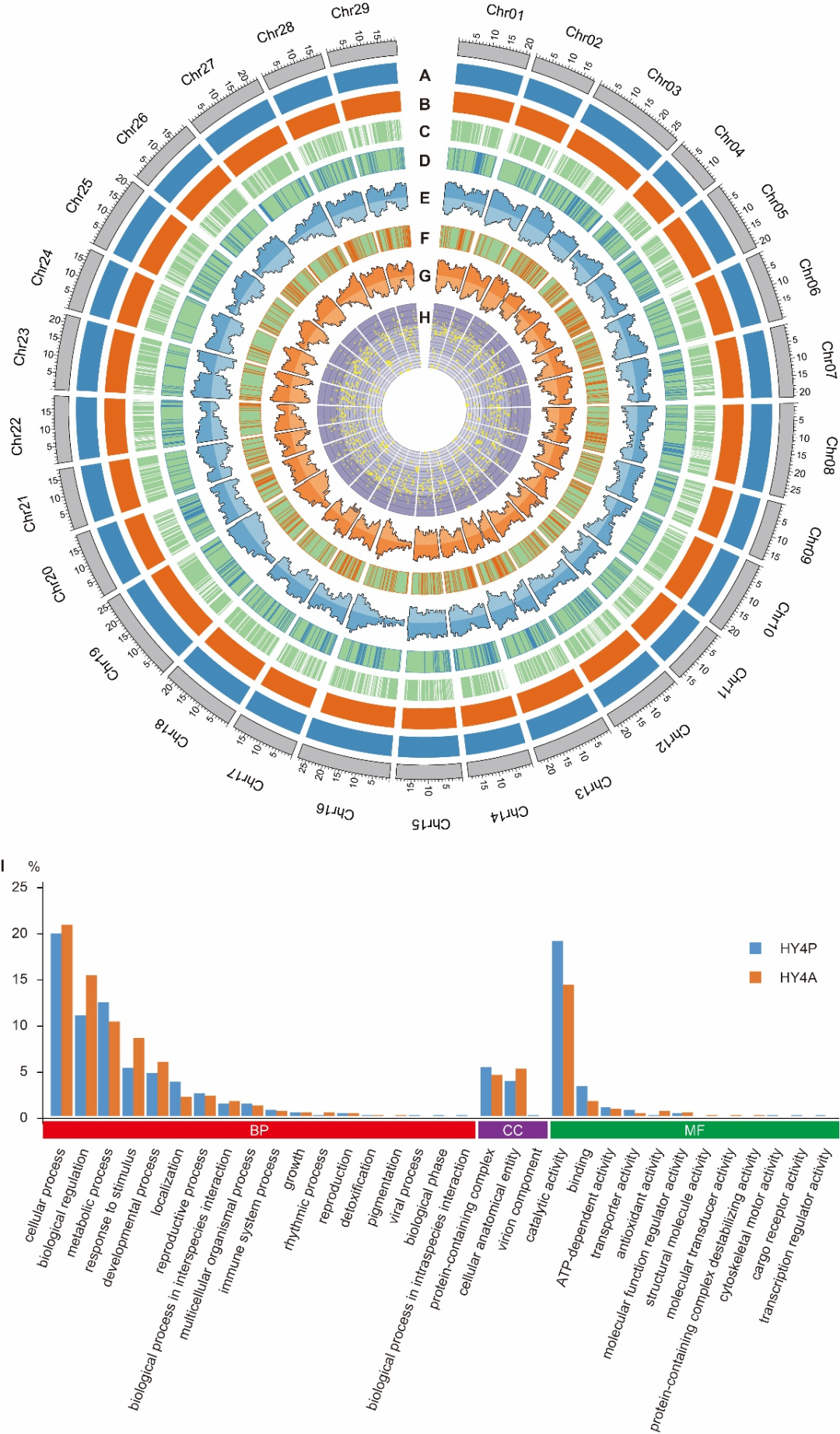
2. T2T基因组的评价
Hongyang v4.0是一个二倍体基因组组合,但两个单倍型的完整性和连续性都优于Hongyang v3.0版本,对此,作者采用多种方法评估了HY4P和HY4A的准确性。BUSCO评估值均高达99.3%,最终组装序列大小分别为606.1和599.6 Mb,注释得到了45,809和45,434个蛋白质编码基因。同时,在HY4P和HY4A中发现的NLR基因数量都远远大于Hongyang v3.0(分别为219、212和151个NLR基因),进一步说明Hongyang v4.0对猕猴桃的功能基因挖掘和分子育种具有很高的应用价值。
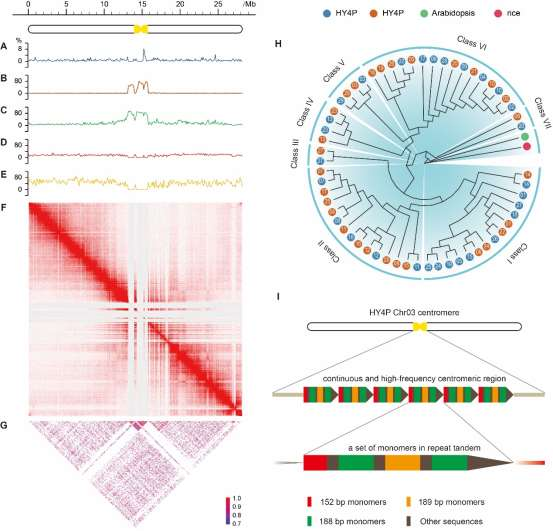
3. 为T2T基因组着丝粒的结构和功能提供验证思路
相较Hongyang v3.0,Hongyang v4.0填补了Hongyang v3.0未组装的全部646个缺口,鉴定了所有58条染色体的着丝粒,组装了除一条染色体中一个末端的所有其他端粒(未组装出来的端粒可能是由于端着丝粒的影响),获得了约为40 Mb的新染色体序列,并修正了历史版本的可能组装错误。在HY4P和HY4A的染色体着丝粒内,分别鉴定有422个和375个蛋白编码基因,并且表明染色体着丝粒不仅在连接一对姐妹染色单体方面发挥物理作用,而且具有参与细胞分裂调控的遗传特征。以拟南芥CEN180和水稻CentO为外群,构建了系统发育树,提示了猕猴桃局部扩张和均质化的适应性过程。
作者介绍:
安徽农业大学园艺学院岳俊阳副教授为该论文的第一/通讯作者,安徽农业大学园艺学院刘永胜特聘教授为论文的最后通讯作者,安徽农业大学园艺学院硕士研究生陈勤瑶、博士研究生王英珍和湖北省农业科学院果树茶叶研究所张蕾副研究员为论文的共同第一作者,合作单位的多位老师和学生参与了本项目的相关工作。
原文链接:
https://doi.org/10.1093/hr/uhac264
扫描查看/下载T2T基因组高分文章合集


